
.jpg)
Genômica e modularidade morfológica: como genes espectadores, sintenia genômica e arrastamento constroem e restringem opções evolutivas emergentes
Michael Crawford
Tradução de Germana Barata
Tenho dois pequenos embriões em espírito, para os quais esqueci
de anotar os nomes, e não sou muito capaz de determinar a qual classe
eles pertencem. Eles poderiam ser lagartos, pequenos pássaros, ou ser
mamíferos muito jovens. O desenvolvimento da cabeça e do tronco ]]>
nesses animais é tão parecida. As extremidades ainda não estão presentes
nesses embriões. Mesmo que elas estivessem presentes nos primeiros
estágios de desenvolvimento, elas não ensinariam nada já que as patas
dos lagartos e mamíferos em desenvolvimento, as asas e patas das aves,
como as mãos e pés das pessoas, possuem a mesma forma básica.
Karl Ernst von Baer (1828)
Em 1979, Gould e Lewontin defenderam uma visão menos reducionista da evolução (1). Eles argumentaram que as teorias dominantes, aquelas que eram centradas no gene (neodarwinistas), colocaram ênfase indevida sobre as características individuais.
Eles sugeriram que tais abordagens tendiam a confundir as consequências indiretas das decisões arquitetônicas com a característica sobre a qual a seleção natural realmente operava. Além disso, eles argumentaram que a "bagagem" de traços ancestrais reduzia a latitude disponível para a inovação morfológica. Este argumento foi posteriormente ampliado por Gould (2). Os recentes avanços na biologia genética faz com que valha a pena rever esse argumento.
Por exemplo, fica claro que as sequências reguladoras de DNA altamente conservadas do genoma se juntam em blocos maiores de regulação que podem expandir-se para englobar diversos genes. Essa tendência enfatiza o grau no qual a herança ancestral desempenha um papel em direcionar e restringir a genética que sustenta a embriogênese e a evolução, respectivamente. Os esforços recentes de sequenciamento indicaram que há um grande número de RNA que são transcritos mas não traduzidos, mas que desempenham um papel na regulação da atividade do gene. Muitos deles são transcritos de forma coordenada a partir de sequências que estão próximas a genes importantes. Juntas, essas descobertas sugerem que uma revisão da evolução, dentro do paradigma e da crítica de Gould e Lewontin, poderia revelar-se útil para iluminar como a modularidade do genoma tornou-se uma propriedade emergente que trabalha sobre a embriogênese e a evolução. Neste artigo, vamos resumir o sucesso do reducionismo, especialmente na definição das operações moleculares que regulam os genes, as células e os tecidos durante a formação do embrião. Nós, então, nos debruçaremos sobre algumas das tentativas mais recentes, holísticas baseadas na fenomenologia, para que grandes conjuntos de dados façam sentido.
Gould e Lewontin usaram uma metáfora poderosa para explicar sua crítica à visão de evolução e desenvolvimento reducionista e centrada no gene (1). A título de exemplo, eles citaram os "rins" (ou, talvez mais corretamente os pendentes) da basílica veneziana de São Marco (Fig. 1). Quando os arquitetos da igreja montaram uma cúpula sobre uma matriz quadrada de arcos de sustentação, havia lacunas deixadas para preencher os cantos. O preenchimento, o qual Gould e Lewontin erroneamente denominaram rins, ocupou, e, em seguida, decorou os espaços nos quais a cúpula não poderia facilmente atingir os cantos quadrados. Uma vez que essas fusões de canto da cúpula tinha sido instaladas e decoradas, impuseram um motivo quadrangular sobre o teto: hipoteticamente, a cúpula poderia ter recebido projetos do mosaico de azulejos que eram 3, 5, 6, 7 ou mais simétricos, no entanto, todas essas opções teriam ressoado mal com os 4 cantos decorados. Com efeito, a decoração e modificação da decisão arquitetônica preliminar - uma cúpula repousada em cima de um quadrado com quatro arcos - estava sendo ditada pelo preenchimento de canto ... o design a posteriori. Em essência, eles argumentaram que pelo menos algumas morfologias poderiam ser consideradas como os acidentes indiretos de decisões antepassadas e arquitetônicas mais primárias, e que essas características acidentais poderiam mais tarde ser utilizadas para alterar e informar modificações da estrutura primária.
]]>

Além disso, Gould e Lewontin (1979) argumentaram que as decisões preliminares e os rins combinados constituem uma "bagagem" de traços ancestrais que restringem a latitude disponível para a inovação morfológica. Gould elaborou, mais tarde, sobre este tema, para sugerir que as restrições não precisam ser consideradas apenas como uma limitação, mas como um ímpeto fornecedor de uma canalização construtiva para a evolução morfológica (2, p.1032). À luz de recentes tentativas de organizar e dar sentido às grandes quantidades de dados decorrentes dos projetos genoma, sua crítica parece ser particularmente perspicaz.
Durante o período de algumas horas ou dias, a célula única de um novo embrião se desenvolve em uma variedade de tipos de células e tecidos extremamente complexos e que sofrem rápidas mudanças. Em estudos de vertebrados tetrápodes, que tomaremos como exemplo, tem havido uma considerável consternação a respeito do como as morfologias emergem e, principalmente, como é que, apesar de grandes diferenças na forma final e função do corpo, esses diferentes animais, parecem todos passar por um estágio embrionário, no qual eles são muito semelhantes. Essa conservação do processo se tornou conhecida como o estágio filotípico e foi observado pela primeira vez por von Baer (3). Uma das causas principais dessa semelhança reside na conservação de genes ancestrais e suas respectivas redes de sinalização - a chamada "homologia profunda" que subjaz a morfogênese. Resumidamente, independentemente de se estar estudando mosca, rã, peixe ou humanos, os genes semelhantes estão direcionando a formação de órgãos e estruturas análogos. Recentemente, ficou evidente que essas redes de genes homólogos estão sendo ampliadas e implantadas de modo imprevisto e que podem ser reveladas através da reinvenção da maneira para a qual olhamos para os dados. Por exemplo, uma abordagem recente sobre a caracterização genética, ou seja, a chamada filoestratigrafia paleogenômica tem aumentado a evidência fornecida pela estrutura do grupo de genes Hox de que os vertebrados são dotados de um plano genérico e robusto de corpo e sobre o qual as morfologias variantes podem ser construídas.
Vamos discutir como as homologias genéticas, sintenias (blocos de genes preservados em conjuntos ordenados ao longo de cromossomos), sequências repetitivas de DNA (que conferem coerência regulatória para genes dentro desses blocos sintênicos), e a implantação de RNAs transcritos não codificantes, ilustram o grau pelo qual a "bagagem" emerge para desempenhar um papel evolutivamente construtivo. Dois temas vão se desenvolver à medida que revelamos essas descobertas. Em primeiro lugar, as abordagens mais antigas da biologia, predominantes até o século XX e que ganharam proeminência na catalogação de dados e na caracterização de regras operacionais gerais, apresentam relevância renovada. A fenomenologia e abordagens holísticas estão ressurgindo como uma estratégia útil para sobreviver ao ataque de esmagamento de dados reducionistas. Em segundo lugar, a modularidade genômica e funcional é emergente e funciona tanto para constranger quanto para canalizar a inovação morfológica.
ARESSURREIÇÃO DAS ABORDAGENS FENOMENOLÓGICAS Quando os investigadores desmontam e estudam as vias de sinalização genéticas e celulares, eles supõem que uma visão atomística de um sistema, em suma, vai aproximar a realidade do todo. Uma das ironias desta abordagem reducionista/neo-darwinista das questões biológicas é que seu próprio sucesso criou conjuntos de dados que são grandes demais para compreender como uma sucessão de partes separadas. Por exemplo, uma única via de transdução de sinal (a cadeia de interações moleculares que liga a recepção de um estímulo na superfície da célula a ativadores que alteram o comportamento de genes específicos) pode envolver dezenas de participantes diretos e muitas dezenas de moderadores adicionais. A dinâmica de uma dessas redes de sinalização pode ser muito difícil, tanto para entender como prever porque a cadeia de causa e efeito não é necessariamente linear. Na verdade, quando se considera que várias redes de sinalização diferentes operam dentro de uma única célula e que colidem cada uma com a outra, a escala de integração e complexidade torna-se aparente.
Imagine o que acontece, então, quando essa complexidade ao nível celular é variada através de comunicações e pressões exercidas entre grupos de células e tecidos. A coordenação e a complexidade da sinalização talvez seja mais complexa no embrião em desenvolvimento do que qualquer outro lugar: a fidelidade na qual nossos corpos são construídos é surpreendente, dadas as variações de desafios metabólicos, ambientais e físicos que podem, e vão, surgir. Novas abordagens para lidar com enormes conjuntos de dados foram criadas, e elas caem na categoria geral da fenomenologia. Geralmente imparcial na abordagem, eles procuram revelar normas gerais de funcionamento e padrões, tanto para categorizar genes, famílias de genes e redes, quanto para buscar motivos repetidos em sequências de DNA, ou através do sequenciamento e comparação de RNAs transcritos em contextos celulares diferentes.
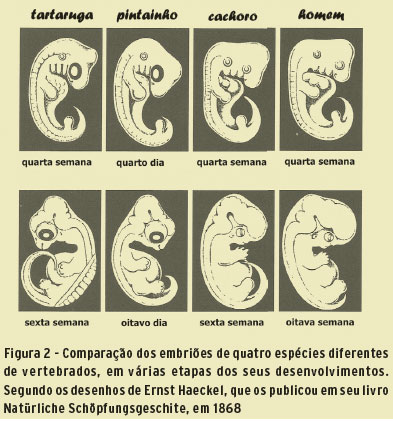
FILOESTRATIGRAFIA Ovos e zigotos (i.e., embriões recentes fertilizados e em divisão), como morfologia de adultos, assumem diversas formas, tamanhos e estratégias de sobrevivência, mas em algum momento eles passam por uma fase em que compartilham semelhanças significativas (3). Haeckel expandiu o estudo dessa homologia morfológica surpreendente para estabelecer as bases para suas teorias da recapitulação (4). Não obstante as críticas feitas por seus contemporâneos (e desde então) acerca da exatidão de suas descrições, um elemento de verdade permanece na disputa de Haeckel que, em algum momento, todos os embriões vertebrados passam por estágios de desenvolvimento, onde se parecem, para o olho destreinado, praticamente idênticos (Figura 2). Por que uma tartaruga, pintinho, cachorro ou embrião humano parecem tão semelhantes em uma determinada fase de desenvolvimento? Qual é a razão e importância desse gargalo de similaridade no projeto de corpo? Será, como Haeckel sugeriu, que "ontogenia é uma repetição curta e rápida da filogenia", ou, em outras palavras, que o desenvolvimento de um embrião tende a recapitular sua história evolutiva (5)? O argumento de Gould e Lewontin sugere que a "bagagem" de herança evolutiva oferece esse plano básico de corpo, mas também que a bagagem impõe limites sobre as inovações morfológicas que podem surgir. Pela mesma razão que a morfologia dessa fase do embrião é conservada no filo, é referida como a etapa filotípica (6). O plano genérico do corpo que se estabelece durante esse processo é criado por um programa de desdobramento da expressão do gene, o zootipo (7). Uma encarnação mais moderna de filotipo define o fenômeno não tanto quanto um ponto discreto no desenvolvimento, mas como uma sucessão ordenada de fases ao longo do tempo- um processo conservado descrito em ressonância direta com Haeckel (8; 9).
]]>
Uma análise imaginativa das categorias de genes expressos ao longo da vida de um organismo foi realizada recentemente (10-12). Cada espécie de gene ativo foi pesquisada e comparada com o banco de dados Genbank e, em seguida, caracterizada com relação a quando, ao longo da evolução, o seu gene parente mais próximo apareceu pela primeira vez. Para cada estágio de desenvolvimento, a idade evolutiva de produtos de genes ativos (transcrições de RNA) identificados poderia ser indexada e uma avaliação derivada para descrever a idade média da evolução dos genes e redes em jogo (denominado filoestratigrafia). Não surpreendentemente, características recentemente adquiridas, aquelas que emergem para explorar oportunidades ambientais específicas, tendem a implantar genes novos. A penetração e dominação de novos nichos ecológicos requer estratégias que afetam a reprodução e fecundação, ou que afetam morfologias e comportamentos juvenil/ adulto. Por outro lado, as redes de genes mais antigas são implantadas ao mesmo tempo que os embriões passam pelo gargalo do filotipo. Em outras palavras, um gene de expressão zootipo impulsiona o filotipo morfológico, e incorpora uma montagem antiga e conservada de genes e redes reguladoras. Mas o que mantém esses genes, redes e processos tão resistentes à mudança?
HOMOLOGIA PROFUNDA: A RETENÇÃO DE GENES ANTIGOS E REDES DE GENES PARA AGENDAR O DESENVOLVIMENTO Os genomas de vertebrados e, de fato, de todos os animais compartilham enormes semelhanças: os números e famílias de genes representados, surpreendentemente, pouco diferencia os seres humanos de vermes ou esponjas. Um exemplo de semelhança comumente citado se manifesta na estrutura do tipo câmara dos olhos entre cefalópodes (polvo e lula), vertebrados e cnidária (água-viva). Essas estruturas se desenvolvem por meios profundamente diferentes, no entanto, durante a padronização, eles constroem órgãos muito semelhantes e implantam genes semelhantes e redes de sinalização, incluindo Opsisn, Cristalinos, Pax, Mitf, Six3 e outros (13-16).
Entre os vertebrados, existem correlações genéticas para o plano do corpo conservado identificado desde o início de 1800. Por exemplo, os vertebrados partilham de um conjunto de ferramentas de genes comuns a outros animais: estes estão contidos dentro das sequências de DNA longas, de aproximadamente 100 mil nucleotídeos, que compõem grupos de cerca de 13 genes Hox que especificam a identidade dos segmentos ou vértebras. Os genes foram secundariamente reimplantados para desempenhar um papel na padronização dos membros em tetrápodes (17). Ao longo do eixo dorsal, os genes Hox são acionados na mesma ordem em que são dispostos no cromossomo, e que progressivamente definem os domínios posteriores do embrião. A modulação da regulação do gene Hox é identificada como uma característica subjacente de inovação morfológica necessárias para gerar vários clusters nos tetrápodes, o elevado grau de interação encaixada e reguladora cruzada, bem como a modularidade de estrutura genômica, tem impedido muito na forma de flexibilidade evolutiva (9; 31). De um modo geral, a conservação da ordem dos genes que é descrita por sintenia (32) provavelmente reflete a necessidade de preservar as estruturas e sequências reguladoras regionais: isso tem implicações interessantes para a montagem de traço(s), a modularidade e a evolução. Eventos de translocação de cromossomos tendem a ser muito raros em comparação a micro-rearranjos, tais como inserções, deleções e inversões, consequentemente as sequências entre os genes podem mudar, mas a ordem linear bruta de genes dentro de segmentos maiores permanece relativamente estática (33). As sequências de DNA não codificantes extremamente conservadas são distribuídas ao longo da extensão de dois milhões ou mais de nucleotídeos, e constituem blocos de regulação do genoma. Por meios ainda não totalmente compreendidos, essas sequências repetitivas ajudam a restringir e regular genes próximos. Blocos regulatórios garantem não apenas que os genes de desenvolvimento e mitóticos se-jam bem coordenados, independentemente da locação onde residem dentro da região, mas também que eles sejam altamente resistentes a amplas mutações substantivas. Na verdade, blocos (18), e isto é corroborado pelos fenótipos atávicos (regressos evolutivos) de alguns ratos Hox mutantes: mutantes podem exibir estruturas do ouvido médio apropriadas aos ancestrais reptilianos, ou eles podem exibir vértebras cervicais no lugar das placas da parte traseira do crânio - adquiridas mais recentemente para conter um cérebro maior (19-25). Essa co-linearidade (26) da localização física do gene e da ordem temporal e espacial da sua expressão é o produto de regulação primorosamente coordenada. As sequências reguladoras para um gene podem ser frequentemente encontradas dentro de um gene vizinho (27), enquanto externamente aos aglomerados de genes (clusters) as sequências reguladoras na parte superior direcionam a expressão co-linear durante o desenvolvimento da coluna vertebral, e as sequências na parte inferior direcionam padrões nos brotos dos membros (28). Para tornar a situação ainda mais complexa, fica claro que as transcrições de RNA não-codificantes (ncRNAs) também desempenham um papel na regulação de genes dentro do cluster. Em moscas, diferentes ncRNAs podem alterar a atividade do gene alvo, atuando tanto em cis ou trans (exercendo uma influência ao lado ou distante do gene) (revisado em 29). Nos mamíferos, os genes ncRNA que estão embutidos dentro do cluster Hox são reguladas de forma coordenada com genes Hox específicos, e eles interagem com as proteínas de remodelação de cromatina, ou produzem miRNAs e longos RNAs não-codificantes que regulam as características de transcrição, tradução e epigenética (o empacotamento do DNA e sua atividade) (29; 30).
SINTENIAS E BLOCOS REGULADORES DE GENOMA Todas as características acima mencionadas já devem ter contribuído para a preservação da estrutura, sequência e atividade de vários grupos de genes Hox durante escalas de tempo evolutivas: apesar das duplicações de genoma regulatórios de genoma podem estar subjacentes à sintenia genômica (34). Até mesmo os resquícios de exons (as sequências de DNA que são transcritas em mRNA), há tempos removidos de seu gene hospedeiro por duplicação mutacional ou eventos de translocação, mantêm a conservação da ordem das sequências se eles residem dentro do blocos regulatórios do genoma (35). Da mesma forma, os desertos de genes adjacentes e genes espectadores se juntam para o percurso - sintenia e modularidade resultam. Em certo sentido, as regiões repetitivas se ligam a genes vizinhos como se fossem vagões de um trem, no qual eles se tornam ativos como uma tropa. Pertinente a essa discussão, muitos dos principais atores do desenvolvimento do olho de vertebrados, como os genes Rax1, Pax6 e Six3, estão imersos dentro de regiões ricas em elementos não codificantes altamente conservados - existe uma esclarecedora utilidade baseada na internet voltada para a identificação de potenciais loci espectadores neste contexto: http://ancora.genereg.net (36). Por exemplo, onde os elementos não codificantes altamente conservados ao redor de Pax6 são particularmente ricos, eles englobam outros oito genes, os quais são expressos, pelo menos, nos olhos e no cérebro. Alguns desses genes espectadores estão associados a mutações oculares (WT1, ELP4, MPPED2). Dito isto, seria preciso ter cuidado em diferenciar os efeitos de mutações associadas a esses genes dos efeitos que suas interrupções possam ter sobre o comportamento regulador de todo o domínio. Isso seria tecnicamente desafiador, porém resolúvel, e poderia ajudar a elucidar a extensão em que esses tímpanos genéticos podem agora influenciar a estrutura maior.
EMERGÊNCIA DE MODULARIDADE GENÔMICA E FUNCIONAL No contexto de agrupamentos de genes sintênicos e blocos de genes regulatórios, a transmissão e carregamento de genes "espectadores", tanto em termos de ligação física quanto da expressão de comportamento, sugere um mecanismo pelo qual a fixação de um traço pode indiretamente comissionar outro. Genes espectadores são aqueles que, como os genes de colágeno fibrilar adjacentes a grupos de genes Hox, são capturados e fixados por restrições regulatórias (cis) em um bloco sintênico. Inicialmente, é provável que os genes espectadores sejam os turistas acidentais de eventos de duplicação ou transposição, mas, no final, passam a desempenhar um novo papel. Vamos examinar, posteriormente, os colágenos fibrilares com mais profundidade. Vou argumentar que esses genes espectadores são como os pendentes de San Marco, e devem ser examinados mais de perto como influências sobre a elaboração da arquitetura dos vertebrados. Quanto mais genes espectadores estiverem envolvidos, e a sintenia estiver consolidada, a modularidade genômica emergente predisporá sistemas para oferecer soluções similares, embora complexas, para os desafios evolutivos. A modularidade pode explicar o quanto animais surpreendentemente diferentes desenvolvem soluções quase idênticas para problemas evolutivos (evolução convergente) através da montagem e reimplantação desses espectadores de bagagem genômica.
A conservação dos blocos sintênicos através da aquisição/evolução de características dispersas não codificantes reguladoras garante tanto a estabilidade, quanto a funcionalidade modular dos genes envelopados. É uma característica interessante da arquitetura biológica que a expansão evolutiva de sequências não codificantes reguladoras força genes vizinhos capturados a expressar padrões semelhantes aos genes que já ocorrem naquele domínio. Um trabalho recente sugere que quanto mais nós de sinalização se formam em uma rede, o número de pontos de controle necessários para limitá-los e direcioná-los, na verdade, diminui (37). Embora seja contra-intuitivo, redes simples, paradoxalmente, exigem mais pontos de controle. Lentamente, enquanto o aparelho de regulação e interação expande-se para incluir mais parceiros, o sistema torna-se mais simples de controlar. Os genes espectadores, situados como estão em um bloco de elementos de regulação em consolidação e ampliação, são cooptados para desempenhar um novo papel: eles enriquecem a agenda que o gene fundador e contexto regulatório originalmente direcionaram. Em pouco tempo, o "espectador" é um jogador, e sua atividade e regulação retroalimentam o todo - um conjunto mais rico de interações emerge para direcionar e construir tecidos, órgãos e processos. A atividade modular da unidade garante que um repertório de ciclos regulatórios e as morfologias consequentes são robustos, mas essa tendência de modular também impõe restrições sobre o panorama das variações do plano corporal, mesmo para filogenias divergentes. No caso de genes Hox, a cooptação de genes de colágeno fibrilar adjacentes para ativar-se, posteriormente, em locais e tempos semelhantes, poderia ter ajudado os antecedentes de vertebrados a transformar-se, a partir de organismos simples segmentados, para organismos com uma coluna vertebral óssea.
]]> Colágenos fibrilares são essenciais para a diferenciação do osso, e o ancestral comum mais antigo da versão dos colágenos fibrilares de vertebrados começou a se desenvolver no momento em que o esqueleto vertebrado surgiu, e antes de um evento de duplicação do genoma inteiro (38). Os clusters Hox, possivelmente como consequência de suas sequências reguladoras a montante ou a jusante, estão organizados em blocos sintênicos compreendendo 19 a 21 genes que residem juntos em vários dos genomas analisados. Entre eles, um grande número de membros do colágeno fibrilar de clade "A" (39). Acredita-se que esses genes de colágeno compartilham os eventos de duplicação do genoma e uma história de arrastamento com seus grupos de genes Hox vizinhos (40). Em um sentido prático, sua localização dentro de um domínio regulatório essencial para a função do grupo ancestral Hox preservou sua ligação física. Como resultado dessa ligação, o seu comportamento também ficou sujeito a influências reguladoras vizinhas: o tempo e padrão espacial de expressão gênica do colágeno fibrilar, acredita-se que deve ter sido ligada ao comportamento do agrupamento gênico Hox (40). Propõem-se que a presença das duas famílias de genes em blocos sintênicos desempenham um papel na evolução do esqueleto dos vertebrados: em um antepassado distante, os complexos de Hox subdividiram o organismo em segmentos discretos, e a subsequente duplicação do genoma completo permitiu que os genes de colágeno adjacentes tivessem uma latitude suficiente para divergir estrutural e funcionalmente e, em seguida, fazer a nucleação da matriz extracelular das células condrogênicas (células de cartilagem). Essas células condrogênicas que expressam colágeno são presumivelmente originadas a partir de uma população ancestral que emergiu da notocorda, onde tanto as famílias do gene Hox e do gene colágeno expressam-se (41; 42) e, posteriormente, as identidades segmentares traduzirem-se em características morfológicas ossificadas, ou seja, as vértebras.Pode ser de suma importância compreender até que ponto os blocos regulatórios dos genes expandem ou contraem em filos diversificados uma vez que isso nos dá alguns insights sobre a importância evolutiva de arrastamento genômico. Para este fim, uma análise de filoestratigrafia de blocos regulatórios do genoma poderia revelar-se útil. Por exemplo, os genes que transmitem características particularmente valiosas e que são fixadas no início da evolução poderiam atuar como centros de nucleação para blocos regulatórios genômicos emergentes. Até que ponto, ao longo da história evolutiva, elementos reguladores não codificantes e altamente conservados, que se avizinham a esses genes críticos, eventualmente se expandiram para abarcar as regiões vizinhas? Considerando o exemplo de órgãos sensíveis à luz já descritos acima, os genes homólogos Pax6 conservados sugerem que o desenvolvimento da visão apenas envolveu arrastamento regulatório e modularização genômica/funcional. Valeria a pena selecionar uma dúzia ou mais de genes importantes para o desenvolvimento e repetir o exercício usando genomas de organismos relacionados de maneira mais distante. Uma investigação para avaliar o papel da modularidade genética em expansão na evolução do plano corporal deveria questionar: será que os blocos sintênicos ao redor de genes importantes, especialmente genes que são fundamentais para a sinalização de nodos, expandem para abranger genes vizinhos úteis (re)implantados?
A MODULARIDADE EMERGENTE AUMENTA A COMPLEXIDADE ENQUANTO RESTRINGE O REPERTÓRIO MORFOLÓGICO Como podemos ver, vários mecanismos estão entrando em cena para tornar modulares o genoma: genes vizinhos estão agrupados em grupos sintênicos que permanecem intactos ao longo de períodos evolutivos significativos. Não apenas os genes são ligados fisicamente, mas também são incorporados em redes reguladoras resistentes à mudança. Além disso, os genes dentro de um cluster podem compartilhar elementos reguladores e ser ativos em tecidos semelhantes e em períodos semelhantes. Esses atributos têm duas consequências. Em primeiro lugar, como previsto por Gould (2), as limitações impostas por essa modularidade ajudam a canalizar a direção da mudança evolutiva. Eles podem dar uma aparência superficial de uma teleologia evolutiva. Em segundo lugar, quando os traços e os genes são reunidos em suítes modulares, os traços produzem morfologias mais complexas, mas o repertório de suítes disponíveis para implantação é limitado. Por exemplo, a sintenia de genes de fatores de crescimento, como o FGF3, 4 e 19 em carnívoros poderia servir como um exemplo. Esses genes se combinam para regular aspectos da morfologia dos membros, da audição, da função da vesícula biliar, e do tamanho do dente canino. Talvez haja uma razão para a qual morfologias corporais semelhantes surjam em carnívoros terrestres tão díspares como os gatos, cachorros e o tilacino marsupial (o chamado tigre da Tasmânia). Será que a modulação do FGF4 é necessária para um forte desenvolvimento dos membros traseiros ligados às alterações na função FGF3 que são necessárias para o crescimento do dente canino (43; 44)? Será que a atividade do FGF19 é necessária para a vesícula biliar e para a função do esfíncter, ligada aos hábitos alimentares intermitentes e aos constrangimentos morfológicos desses carnívoros (45; 46)? Valeria a pena verificar se as marcas de blocos de regulação do genoma e circuitos reguladores não codificantes de RNA estão presentes nessas três classes e famílias diferentes de mamíferos. A aglomeração emergente de genes e processos genéticos de desenvolvimento em módulos funcionais podem acabar provocando mais ímpeto e constrangimentos às "homologias profundas" do que se acreditava anteriormente.
Michael Crawford é doutor pela Universidade de Toronto, concluiu seus estudos de pós-doutorado na Universidade McGill e no Instituto de Pesquisas Clínicas de Montreal. Atualmente é professor associado do Departamento de Ciências Biológicas, da Universidade de Windsor, no Canadá, e recebeu apoio do Conselho de Pesquisa em Ciências Naturais e Engenharia (NSERC) do Canadá.
NOTAS E REFERÊNCIAS BIBLIOGRÁFICAS
1. S. J. Gould; R. C. Lewontin, Proc R Soc Lond B Biol Sci 205, 581 (1979).
2. S. J. Gould, The structure of evolutionary theory. Belknap Press of Harvard University Press, Cambridge, Mass., 2002, pp. xxii, 1433 p.
3. K. E. v. Baer, Über Entwickelungsgeschichte der Thiere Beobachtungund Reflexion. (Den Gebrüdern Bornträger, Königsberg, 1828).
4. E. H. P. A. Haeckel, Generelle morphologie der organismen allgemeinegrundzüge der organischen formen-wissenschaft: mechanischbegründet durch die von Charles Darwin reformirte Descendenz-Theorie., (G. Reimer., Berlin 1866).
5. L. W. Swan, BioScience 40, 376 (1990).
6. K. Sander, in Development and evolution, B. C. Goodwin, N. Holder, C. C. Wylie, Eds. Cambridge University Press, Cambridge Cambridgeshire; New York, 1983, pp. 137-159.
7. J. M. Slack; P. W. Holland; C. F. Graham. Nature, 361, 490 (Feb 11, 1993).
8. P. Alberch, M. J. Blanco, Int. J. Dev. Biol., 40, 845 (Aug, 1996).
9. D. Duboule. Dev. Suppl., 135 (1994).
10. T. Domazet-Loso; J. Brajkovic; D. Tautz. Trends Genet., 23, 533 (Nov, 2007).
11. T. Domazet-Loso; D. Tautz. Genome Res., 13, 2213 (Oct, 2003).
12. T. Domazet-Loso; D. Tautz. Nature, 468, 815 (Dec 9, 2010).
13. Z. Kozmik et al. Proc. Nat. Acad. Sci. USA, 105, 8989 (Jul 1, 2008).
14. Z. Kozmik et al. Dev. Cell., 5, 773 (Nov, 2003).
15. S. I. Tomarev. Int. J. Dev. Biol., 41, 835 (Dec, 1997).
16. S. I. Tomarev et al. Proc. Nat. Acad. Sci. USA, 94, 2421 (Mar 18, 1997).
17. J. Zakany; D. Duboule. Curr. Opin. Genet. Dev., 17, 359 (Aug, 2007).
18. F. H. Ruddle et al. Ann. NY Acad. Sci., 870, 238 (May 18, 1999).
19. B. K. Hall. Nat. Genet., 10, 126 (1995).
20. F. M. Rijli; P. Dolle; V. Fraulob; M. LeMeur; P. Chambon. Dev. Dyn., 201, 366 (1994).
21. F. M. Rijli et al. Cell, 75, 1333 (1993).
22. M. Gendron-Maguire; M. Mallo; M. Zhang; T. Gridley. Cell, 75, 1317 (1993).
23. M. Kessel; R. Balling; P. Gruss. Cell, 61, 301 (1990).
24. G. S. B. Horan et al., in Mouse Molecular Genetics. Cold Spring Harbor, New York, 1994.
25. B. G. Condie; M. R. Capecchi. Development, 119, 579 (1993).
26. Co-linearidade é o termo técnico usado para descrever como a distribuição espacial de genes Hox em um cromossomo se reflete também na distribuição espacial de seus respectivos produtos gênicos ao longo da axis antero-posterior do embrião de moscas, bem como, adicionalmente, ao tempo de suas atividades em vertebrados.
27. D. Duboule. Curr. Opin. Genet. Dev., 8, 514 (Oct, 1998).
]]>28. J. Deschamps. Curr. Opin. Genet. Dev., 17, 422 (Oct, 2007).
29. H. W. Brock; J. W. Hodgson; S. Petruk; A. Mazo. Biochem. Cell. Biol., 87, 27 (Feb, 2009).
30. D. Lemons; W. McGinnis. Science, 313, 1918 (Sep 29, 2006).
31. D. Duboule. Development, 134, 2549 (Jul, 2007).
32. Sintenia é a preservação da ordem linear de genes ao longo dos segmentos cromossômicos que são adquiridos de um ancestral comum e que são compartilhados por espécies diferentes. Embora o número, tamanho, e orientação dos cromossomos possa variar entre diferentes especies, os sub-domínios permanecem de serem comparados diretamente.
33. H. Kikuta et al., Genome Res 17, 545 (May, 2007).
34. P. G. Engstrom; ,S. J. Ho Sui; O. Drivenes; T. S. Becker; B. Lenhard. Genome Res. 17, 1898 (Dec, 2007).
35. X. Dong et al. Nucleic Acids Res., 38, 1071 (Mar, 2010).
36. P. G. Engstrom; D. Fredman; B. Lenhard. Genome Biol., 9, R34 (2008).
37. Y. Y. Liu; J. J. Slotine; A. L. Barabasi. Nature, 473, 167 (May 12, 2011).
38. R. P. Boot-Handford; D. S. Tuckwell. Bioessays, 25, 142 (Feb, 2003).
39. A. P. Lee; E. G. Koh; A. Tay; S. Brenner; B. Venkatesh. Proc. Nat. Acad.Sci. USA, 103, 6994 (May 2, 2006).
40. W. J. Bailey; J. Kim; G. P. Wagner; F. H. Ruddle. Mol. Biol. Evol., 14, 843 (Aug, 1997).
41. G. Zhang; M. J. Cohn. Curr. Opin. Genet. Dev., 18, 387 (Aug, 2008).
42. V. E. Prince, A. L. Price, R. K. Ho, Dev Genes Evol 208, 517 (Nov, 1998).
43. H. G. Parker et al., Science 325, 995 (Aug 21, 2009).
44. C. Y. Gregory-Evans et al., Hum Mol Genet 16, 2482 (Oct 15, 2007).
45. F. W. Gorham, A. C. Ivy, General function of the gall bladder from theevolutionary standpoint. (Chicago,, 1938), pp. 1 p.l., p.
46. M. Choi et al., Nat Med 12, 1253 (Nov, 2006).
]]>